HOME > 研究紹介
研究紹介と成果
私たちはこれまで、ゲノム編集技術をマウスおよびラットの受精卵に利用することで、効率的な新規遺伝子改変技術の開発、新しいモデル動物の作製を行ってきました。これらを利用することで、特定遺伝子の発現場所や時期を制御したコンディショナルKO、モデル動物のゲノムをヒト特異的DNA配列に置き換えた”ゲノムヒト化動物”などが効率的に作製できます。
ゲノム編集センターでは、このように新しく開発した技術や培ってきたノウハウを生かして、ゲノム編集に関連した解析やモデル動物作製支援を行っています。これからも様々な技術開発を行い、汎用性の高いゲノム編集技術を研究者の方々へ提供していく予定です。
研究1:一本鎖オリゴDNAを活用した効率的ノックイン法の確立
ノックイン動物の作製は、Cas9およびgRNAに加えて、相同配列を持つドナーDNAを受精卵に同時に導入する必要があります。このドナーDNAには、プラスミドDNAと一本鎖オリゴDNAが主に用いられていますが、私たちは、一本鎖オリゴDNAを活用した効率的なノックイン法を確立し、さらに従来に比べて大きいサイズを導入できる手法も開発しました。
(1)複数の配列パターンについて、一本鎖オリゴDNAをドナーとして用いることで効率的にノックイン動物を作成できることを示してきました。また、Nickaseを用いることで長鎖一本鎖DNAを得ることに成功し、ノックインのドナーDNAに利用することで、これまでGFP等のタグ化、Floxed等のコンディショナルKOなど、様々なタイプのノックイン動物の作製に成功しています。
(2)一本鎖オリゴDNAを介した新しいプラスミドノックイン法、2ヒット2オリゴ法(2H2OP法)を開発しました。この方法では、CRISPR/Cas9が「はさみ」として、また二本の一本鎖オリゴDNAが「のり」として働き、プラスミドDNAを特定のゲノム上に正確にノックインすることが可能となります。実際に2H2OP法を用いて、CAG-GFPプラスミドのノックイン、BACプラスミドを用いたノックインにも成功しました。

A.一本鎖オリゴDNAを用いた毛色遺伝子のノックインラット
(オンマウスで拡大)
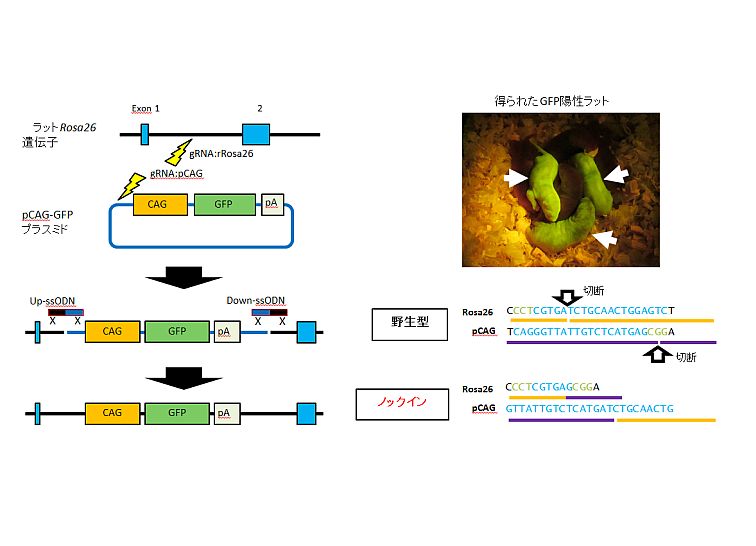
B.新規プラスミドDNAノックイン法(2H2OP法)を用いたGFPノックインラットの作製 (オンマウスで拡大)
ノックイン技術の効率化は、外来遺伝子の安定的導入に加え、内在性遺伝子の詳細な機能解析、特に発現部位や発現時期の操作、ライブイメージング等が可能になり、研究におけるモデル動物の有用性が非常に高まります。
Nature Communications. 7, 10431, 2016
in rats using the CRISPR-Cas platform
Nature Communications. 5:4240, 2014
研究2:エレクトロポレーション法を用いたノックイン動物作製の簡易化
CRISPRコンポーネントの受精卵への導入法は、従来のトランスジェニック動物と同じく、顕微鏡下でガラス針から注入するマイクロインジェクション法が主流です。この方法は確実に受精卵内へ導入することができる一方で、熟練した技術と高価な設備が必要なため、使用できる研究室は限られています。
私たちは、エレクトロポレーション法を用いて受精卵に電気パルスを当てることで、微細な穴をあける導入法を確立し、従来よりも少ない設備で簡単にマウスやラットのゲノム編集ができることを示しました。この方法は、一度に最大100個程度の受精卵にDNAやRNAを導入できます。また長鎖の一本鎖DNAを組み合わせることで比較的大きい配列(GFP、Flox)を、エレクトロポレーションを用いてノックインすることにも成功しています。

スーパーエレクトロポレーター NEPA21
(ネッパジーン株式会社)
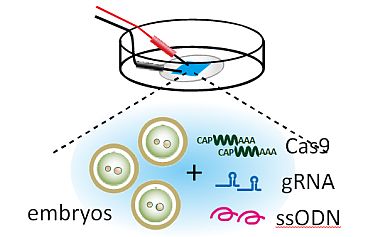
エレクトロポレーション法を用いた遺伝子改変動物の作製
Hiraoka Y, Takemoto N, Tanaka T, Ooguchi Y, Skehel P, Aida T, Takeda J, Mashimo T
BMC Genomics. 19(1):318. 2018
PLoS One. 10(11):e0142755. 2015
Scientific Reports. 4:6382. 2014
参考資料